CRISPR e Lievito: Il Kit Rivoluzionario per Produrre Proteine su Misura in Komagataella phaffii
Ciao a tutti, appassionati di scienza e biotecnologie! Oggi voglio parlarvi di qualcosa che mi entusiasma parecchio: un nuovo “kit degli attrezzi” che abbiamo messo a punto per lavorare con un lievito davvero speciale, *Komagataella phaffii*, che forse molti conoscono con il suo vecchio nome, *Pichia pastoris*. Questo microrganismo è una vera superstar nel mondo delle biotecnologie, soprattutto quando si tratta di produrre proteine ricombinanti, incluse quelle alimentari di origine vegetale o animale. Pensate che diverse proteine prodotte così sono già state approvate per il mercato USA!
Perché *K. phaffii* è così speciale?
Questo lievito è fantastico per diversi motivi:
- Ha una capacità incredibile di secernere proteine all’esterno della cellula.
- Produce pochissime proteine proprie, il che rende la purificazione di quella che ci interessa molto più semplice.
- È capace di fare modifiche post-traduzionali simili a quelle degli organismi superiori.
- Esiste un’ampia gamma di strumenti molecolari per manipolarlo geneticamente.
Questa tecnica, chiamata “fermentazione di precisione”, è vista come una delle chiavi per il futuro degli ingredienti proteici nei nostri alimenti.
Le sfide dell’ingegneria genetica tradizionale
Finora, per far produrre a *K. phaffii* la proteina desiderata, si usavano spesso vettori integrativi che si inserivano nel genoma. Il problema? Questi metodi richiedono l’uso di marcatori di selezione (come geni di resistenza agli antibiotici, un “no-go” per il cibo, o geni che rendono il lievito dipendente da nutrienti specifici, rallentandone la crescita). Inoltre, l’integrazione avveniva un po’ a caso e con un numero variabile di copie del gene inserito, costringendoci a uno screening lungo e laborioso per trovare i cloni “giusti”. Un vero terno al lotto!
L’arrivo di CRISPR/Cas9: la svolta?
Qui entra in gioco la tecnologia CRISPR/Cas9, le famose “forbici molecolari”. Questo sistema permette di tagliare il DNA in punti precisissimi, guidato da una molecola chiamata sgRNA. Fornendo poi un “modello” di DNA (il nostro gene d’interesse con delle sequenze di aggancio), possiamo indurre la cellula a riparare il taglio inserendo esattamente ciò che vogliamo, dove vogliamo. E la cosa fantastica è che, se fatto bene, il processo è così efficiente da non richiedere più i marcatori di selezione! Un’integrazione “pulita” e precisa.
Tuttavia, anche CRISPR ha le sue sfide: non tutti i siti bersaglio nel genoma funzionano allo stesso modo, e trovare quelli più efficienti richiede un po’ di lavoro. Inoltre, bisogna identificare siti di integrazione “neutri”, che non danneggino il lievito e permettano una buona espressione del gene inserito.
Il nostro Toolkit: GoldenPiCS incontra CRISPR
Per rendere tutto più semplice e standardizzato, abbiamo pensato di adattare un sistema di clonaggio modulare già esistente, chiamato GoldenPiCS. Questo sistema usa la tecnica “Golden Gate”, che permette di assemblare diversi pezzi di DNA (promotore, gene, terminatore) in modo preciso e veloce, come dei mattoncini LEGO.
La nostra idea è stata quella di combinare la flessibilità di GoldenPiCS con la precisione di CRISPR/Cas9. Abbiamo quindi creato:
- Plasmidi Cas9/sgRNA: Contengono le “forbici” Cas9 e la “guida” sgRNA specifica per tagliare in tre siti genomici promettenti (chiamati 04576, PFK1 e ROX1), identificati come neutri ed efficienti in studi precedenti.
- Plasmidi “Donor Helper”: Sostituiscono l’ultimo passaggio del sistema GoldenPiCS originale. Questi plasmidi contengono le sequenze di omologia necessarie per l’integrazione precisa nel sito target tramite CRISPR e i siti di clonaggio Golden Gate per inserire facilmente la nostra “cassetta di espressione” (il gene d’interesse con promotore e terminatore).
In pratica, ora possiamo assemblare la nostra cassetta di espressione con GoldenPiCS e poi usare il plasmide donor helper corrispondente insieme al plasmide CRISPR specifico per inserirla nel genoma di *K. phaffii* in modo mirato e senza marcatori.
Mettiamo alla prova il sistema: il test con eGFP
Per vedere quanto funzionasse bene il nostro toolkit, abbiamo usato come “reporter” una proteina fluorescente verde (eGFP). Abbiamo costruito le cassette di espressione per eGFP e le abbiamo integrate nei tre siti target (04576, PFK1, ROX1).
Cosa abbiamo scoperto?
- Efficienza di trasformazione (quanti cloni ottenevamo in totale): Il sito ROX1 è stato il campione, dandoci il maggior numero di trasformanti. Il sito 04576 è stato il più “difficile” da questo punto di vista.
- Efficienza di integrazione (quanti dei cloni ottenuti avevano effettivamente integrato eGFP, diventando fluorescenti): Qui la situazione si è ribaltata! Il sito 04576 ha mostrato la più alta percentuale di cloni fluorescenti (in media il 66%), mentre PFK1 è stato il meno efficiente.
Questo ci dice che c’è un certo compromesso: ROX1 dà più cloni totali, ma una frazione minore è quella “giusta”; 04576 dà meno cloni, ma una percentuale maggiore ha l’integrazione corretta. Interessante, vero? Abbiamo anche notato che lasciare le cellule “riprendersi” un po’ più a lungo (3 ore invece di 1) dopo l’elettroporazione (la tecnica per far entrare il DNA) tendeva a migliorare leggermente i risultati.
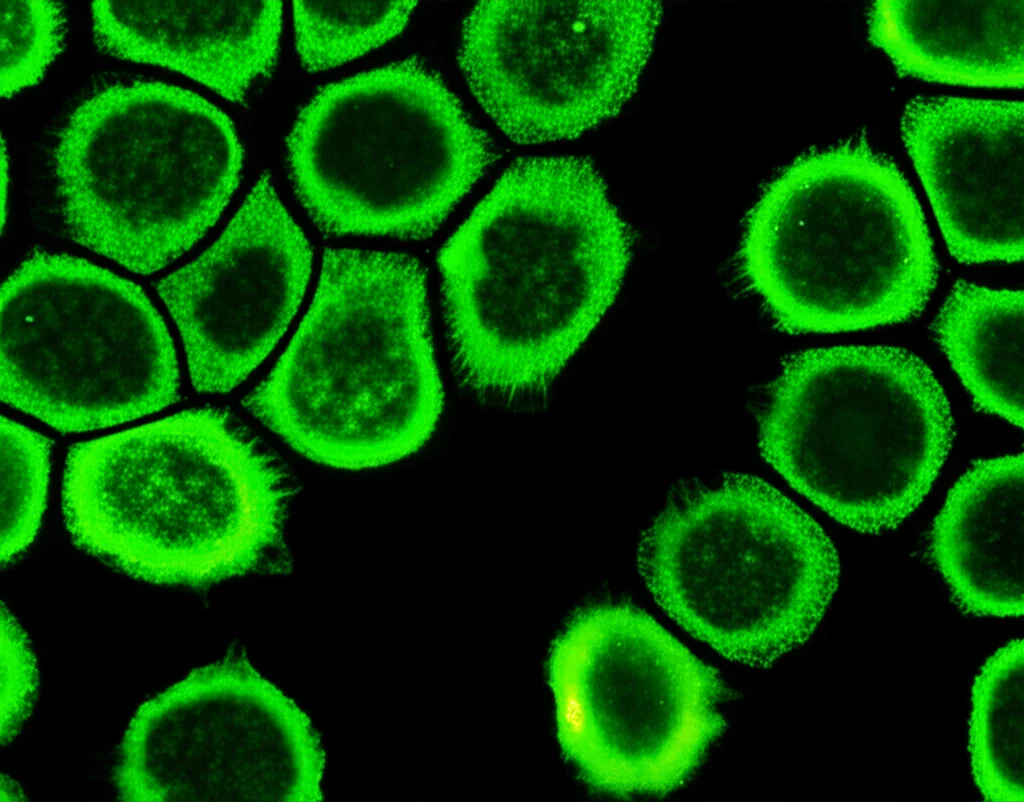
Analisi approfondita: cosa ci dice il genoma (WGS)?
Osservando i cloni fluorescenti, abbiamo notato una grande variabilità nei livelli di fluorescenza. Alcuni brillavano poco, altri moltissimo. Questo ci ha fatto sospettare che il numero di copie della cassetta eGFP integrate potesse variare.
Per vederci chiaro, abbiamo selezionato alcuni cloni con fluorescenza bassa, media e alta per ogni sito di integrazione e abbiamo sequenziato il loro intero genoma (Whole Genome Sequencing – WGS). E qui sono arrivate le sorprese!
- Numero di copie variabile: Come sospettavamo, i cloni con fluorescenza più alta avevano effettivamente integrato multiple copie della cassetta eGFP. Addirittura, un clone nel sito 04576 sembrava averne ben 14! Il sito PFK1 tendeva ad avere meno copie multiple rispetto agli altri due.
- Intrusi indesiderati: In molti cloni con copie multiple, abbiamo trovato anche pezzi del plasmide “backbone” (la parte del plasmide donor helper che non dovrebbe integrarsi, contenente ad esempio il gene di resistenza per E. coli). Sembra che i frammenti di DNA linearizzati (tagliati con l’enzima EcoRI prima della trasformazione) si siano “ricuciti” insieme in modo casuale all’interno della cellula prima o durante l’integrazione. Un fenomeno noto come *in vivo ligation*.
- Nessuna integrazione fuori bersaglio: La buona notizia è che non abbiamo trovato prove di integrazioni in punti casuali del genoma. Il sistema CRISPR sembra aver funzionato bene nel dirigere l’inserzione solo nei siti voluti.
- Un problema al sito ROX1: In un clone ROX1 con fluorescenza media, abbiamo scoperto la perdita di un pezzo significativo del cromosoma (circa 36.600 basi!) vicino al sito di integrazione. Questo ha causato una crescita più lenta del lievito. Altri cloni ROX1 mostravano pattern di crescita simili, suggerendo che questo problema potesse non essere isolato per quel sito specifico, forse a causa della sua vicinanza all’estremità del cromosoma.
- Correlazione non lineare: Curiosamente, l’aumento della fluorescenza non era sempre direttamente proporzionale al numero di copie stimato. Ad esempio, un clone con 14 copie non brillava 14 volte di più di uno con una copia. Questo suggerisce che, oltre un certo numero di copie, altri fattori (come la capacità della cellula di produrre e secernere la proteina) diventano limitanti.

Applicazione reale: produrre ovalbumina (la proteina dell’uovo)
Bello giocare con la fluorescenza, ma il nostro obiettivo era produrre proteine utili, specialmente per l’industria alimentare. Abbiamo quindi deciso di testare il sistema per produrre ovalbumina, la principale proteina dell’albume d’uovo, molto importante per le sue proprietà nutrizionali e funzionali.
Abbiamo costruito una cassetta di espressione per il gene dell’ovalbumina di pollo, aggiungendo una sequenza segnale (α-MF di *S. cerevisiae*) per indirizzarla alla secrezione fuori dalla cellula. Abbiamo scelto il sito 04576, che aveva dato la migliore efficienza di integrazione con eGFP.
Il risultato? Successo! Siamo riusciti a ottenere cloni di *K. phaffii* che producevano e secernevano ovalbumina nel mezzo di coltura. Analizzando le proteine secrete, abbiamo visto due bande principali (di circa 45 e 47 kDa), probabilmente dovute a diversi pattern di glicosilazione (l’aggiunta di zuccheri alla proteina), un fenomeno già osservato in altri studi. La produzione media è stata di circa 35 mg per litro di coltura. Non sono livelli altissimi rispetto ad altri sistemi ottimizzati, ma è una prova di concetto importante: il nostro toolkit CRISPR/GoldenPiCS funziona anche per proteine complesse e secrete di interesse alimentare. E, per quanto ne sappiamo, è la prima volta che CRISPR/Cas9 viene usato per produrre ovalbumina ricombinante in microrganismi!

Cosa ci portiamo a casa e prossimi passi
Questo lavoro dimostra che combinare la modularità di Golden Gate con la precisione di CRISPR/Cas9 è una strategia potente ed efficiente per l’ingegneria genetica di *K. phaffii*. Il nostro toolkit permette un’integrazione markerless (senza marcatori) e mirata di cassette di espressione.
Abbiamo però anche identificato delle sfide:
- La tendenza a ottenere integrazioni multiple e l’inclusione di frammenti del plasmide backbone, probabilmente a causa della ligazione *in vivo* delle estremità coesive generate dal taglio con EcoRI.
- La possibilità di riarrangiamenti cromosomici o delezioni, come quella osservata nel sito ROX1.
Questi aspetti andranno affrontati in futuro. Ad esempio, si potrebbe trattare il DNA donatore prima della trasformazione per eliminare le estremità coesive, o purificare la cassetta di interesse via gel o PCR per rimuovere il backbone. Sarà anche importante verificare sempre l’integrità genomica dei cloni ottenuti, magari usando tecniche di sequenziamento a lettura lunga (long-read sequencing) per scovare meglio eventuali riarrangiamenti.
Nonostante queste sfide, il potenziale è enorme. Questo approccio apre le porte a una produzione più efficiente e “pulita” di una vasta gamma di proteine ricombinanti di alto valore, dalle applicazioni farmaceutiche a quelle alimentari, usando *K. phaffii* come fabbrica cellulare. Il futuro della fermentazione di precisione sembra ancora più brillante!
Fonte: Springer