Nanoparticelle Intelligenti Ispirate alla Clorochina: La Mia Scommessa per Rivoluzionare la Terapia Genica!
Amici scienziati e curiosi di scoperte, oggi voglio portarvi con me in un viaggio affascinante nel mondo delle nanotecnologie e della terapia genica. Immaginate di poter “consegnare” istruzioni genetiche direttamente alle cellule, come un postino super efficiente che sa esattamente dove andare e come superare ogni ostacolo. Ecco, questo è un po’ il sogno che inseguiamo quando parliamo di terapie a mRNA e editing genomico.
Negli ultimi anni, l’mRNA ha fatto faville, soprattutto con i vaccini anti-COVID-19, dimostrando un potenziale enorme che va ben oltre la prevenzione delle malattie infettive. Pensate alla possibilità di usarlo per sostituire geni difettosi, combattere il cancro con l’immunoterapia o correggere errori nel nostro DNA. Fantascienza? Non proprio, ma c’è un “ma”.
La Sfida Nascosta: L’Evasione Endosomiale
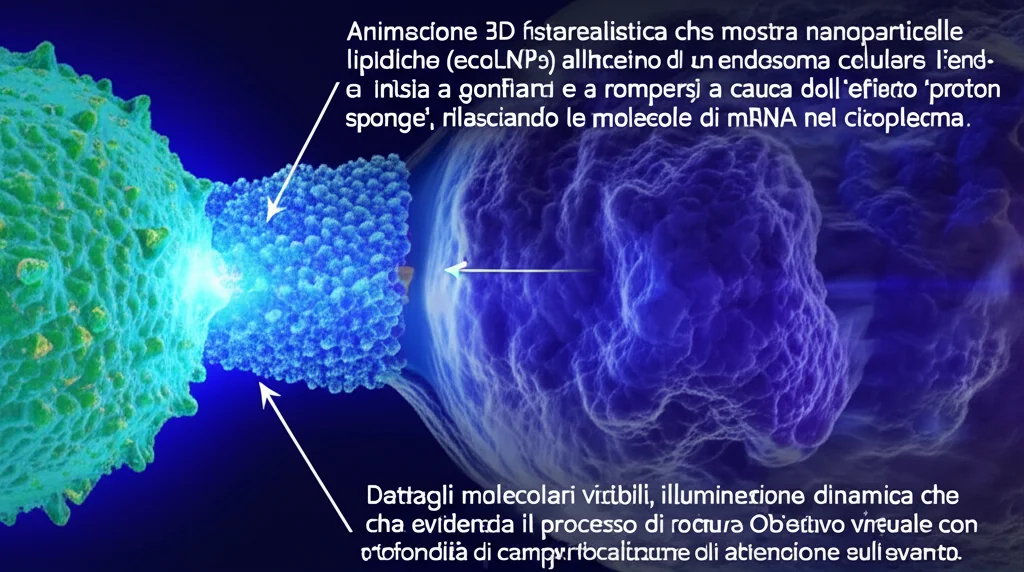
L’mRNA è una molecola tanto potente quanto delicata. È instabile e il nostro corpo è bravissimo a riconoscerlo come “estraneo” e a distruggerlo. Per questo, abbiamo bisogno di “veicoli” speciali, come le nanoparticelle lipidiche (LNP), che lo proteggano e lo aiutino a entrare nelle cellule. Fin qui, tutto bene. Il problema sorge una volta dentro: le LNP con il loro prezioso carico di mRNA vengono inglobate in piccole vescicole chiamate endosomi. Se l’mRNA non riesce a “scappare” da questi endosomi e a raggiungere il citoplasma, dove può fare il suo lavoro, la sua efficacia crolla drasticamente. Questa “evasione endosomiale” è una delle sfide più grandi e, vi assicuro, frustranti!
Si stima che, anche con le LNP più avanzate, solo una piccolissima percentuale di mRNA (forse il 2%!) riesca effettivamente a fuggire. Per le terapie che richiedono alti livelli di espressione proteica, questo è un ostacolo enorme.
L’Ispirazione Inattesa: la Clorochina
E se la soluzione, o almeno parte di essa, fosse nascosta in un vecchio farmaco antimalarico? Parlo della clorochina, un medicinale usato da decenni e presente nella lista dei farmaci essenziali dell’OMS. Oltre alla malaria, la clorochina è usata per malattie reumatiche e si sta studiando per applicazioni antivirali e antitumorali. La cosa che ci ha incuriosito è la sua capacità, osservata in vitro, di potenziare la consegna di acidi nucleici. Come? Beh, la clorochina è una base debole che, una volta entrata negli endosomi (che hanno un pH acido), si protona e rimane intrappolata, destabilizzando la membrana endosomiale o creando pori, aiutando così le molecole co-consegnate a uscire. Un vero e proprio “grimaldello” molecolare!
Da qui, l’idea: e se potessimo integrare le caratteristiche strutturali chiave della clorochina direttamente nei lipidi che formano le nostre nanoparticelle? Nasce così il progetto delle ecoLNP, ovvero “endosomolytic chloroquine-like optimized lipid nanoparticles”. Un nome un po’ lungo, lo so, ma che racchiude l’essenza della nostra scommessa!
Progettare e Ottimizzare: Nascono le ecoLNP
Ci siamo messi al lavoro, scomponendo idealmente la struttura della clorochina in tre “mattoncini”: uno scaffold (l’anello di chinolina), un linker (una catena che collega) e delle code lipidiche (parti idrofobiche). Combinando questi mattoncini in modi diversi, abbiamo creato una libreria di nuovi lipidi “simil-clorochina” (Cll – Chloroquine-like lipids). È stato un lavoro meticoloso, quasi da sarti molecolari!
Abbiamo testato questi nuovi lipidi per la loro capacità di veicolare mRNA che codifica per l’enzima luciferasi (FLuc mRNA) in cellule 293T. Dopo una prima selezione, abbiamo usato una metodologia statistica potente, il Central Composite Design (CCD), per ottimizzare la formulazione delle LNP, giocando con le proporzioni dei vari componenti: il nostro lipide Cll, l’mRNA, lipidi helper (DOPE), colesterolo e lipidi PEGilati. Immaginate di dover trovare la ricetta perfetta per una torta, variando le quantità di farina, uova, zucchero e burro: il CCD ci aiuta a farlo in modo sistematico.
Dopo vari cicli di ottimizzazione e screening, è emerso un “campione”: il lipide CF3-2N6-UC18. Questo lipide, combinato nelle giuste proporzioni con gli altri componenti, forma le nostre ecoLNP. Queste nanoparticelle hanno mostrato un’efficienza di incapsulamento dell’mRNA del 98%, una forma sferica con un diametro di circa 200 nm e una buona stabilità, soprattutto se conservate a 4°C (in condizioni non congelate, mantengono la loro potenza per almeno una settimana!).
Le ecoLNP alla Prova dei Fatti: Efficienza e Versatilità
Ma quanto sono brave queste ecoLNP a consegnare l’mRNA? Beh, parecchio! In vitro, si sono dimostrate fino a 18.9 volte più potenti dei reagenti di trasfezione commerciali come Lipofectamine 2000 e 4.4 volte più di Lipofectamine MessengerMAX. E non solo con l’mRNA della luciferasi: abbiamo ottenuto ottimi risultati anche con mRNA per la proteina fluorescente verde (eGFP), mCherry e la β-galattosidasi.
Una delle cose più entusiasmanti è che le ecoLNP funzionano bene anche con cellule “difficili da trasfettare”, come le cellule monocitiche umane THP-1 e persino in colture cellulari 3D, che mimano meglio la complessità dei tessuti. Immaginate di vedere l’intera struttura 3D illuminarsi di verde o rosso grazie all’mRNA consegnato! Non solo: le ecoLNP si sono dimostrate capaci di veicolare anche altri tipi di acidi nucleici, come siRNA (ottenendo un silenziamento genico superiore all’85%) e DNA plasmidico.
Un aspetto cruciale è la protezione del carico. L’mRNA nudo verrebbe degradato in pochi minuti da siero o RNasi. Le nostre ecoLNP, invece, proteggono l’mRNA per oltre 6 ore! E per quanto riguarda la sicurezza? I test di emolisi hanno mostrato che a pH fisiologico (circa 7.4) le ecoLNP sono biocompatibili, mentre a pH più acido (5.4), simile a quello degli endosomi, mostrano un’attività emolitica, suggerendo la loro capacità di disgregare le membrane endosomiali. Un comportamento pH-sensibile, proprio quello che cercavamo!
Come Fanno le ecoLNP a “Scappare”? I Meccanismi d’Azione
Abbiamo cercato di capire più a fondo come funzionano. L’internalizzazione delle ecoLNP nelle cellule coinvolge molteplici vie endocitiche, in particolare la macropinocitosi, ed è un processo che richiede energia. L’inibizione delle pompe protoniche con Bafilomicina A1 blocca quasi del tutto l’ingresso o la fuga, suggerendo un ruolo chiave del pH.
Due meccanismi sembrano essere i protagonisti dell’efficace fuga endosomiale delle ecoLNP:
- Effetto spugna protonica (Proton Sponge Effect): Il nostro lipide CF3-2N6-UC18, grazie ai suoi atomi di azoto ionizzabili (ereditati dalla struttura simil-clorochina), può assorbire protoni all’interno degli endosomi acidi. Questo “tamponamento” richiama acqua e ioni, causando il rigonfiamento e la rottura della vescicola endosomiale, liberando l’mRNA. Abbiamo confermato questo effetto misurando un aumento del pH endo-lisosomiale nelle cellule trattate con ecoLNP.
- Disfunzione della membrana promossa dalla Sapoina B (SapB): La Saposina B è una proteina lisosomiale che lega i lipidi e interagisce con la clorochina. Simulazioni al computer (docking molecolare) hanno mostrato che il nostro lipide CF3-2N6-UC18 si lega alla SapB in modo simile alla clorochina. Un lipide di controllo, privo dell’anello di chinolina caratteristico (PNT-2N6-UC18), pur entrando nelle cellule, mostrava una scarsa traduzione dell’mRNA e rimaneva intrappolato negli endosomi. Questo suggerisce che l’interazione con SapB, facilitata dalla struttura chinolinica, potrebbe promuovere la fusione o la destabilizzazione delle membrane endo-lisosomiali.
Esperimenti con traccianti fluorescenti hanno confermato visivamente questa fuga: mentre l’mRNA veicolato dal lipide di controllo rimaneva confinato in puntini luminosi (gli endosomi), quello veicolato dalle ecoLNP si diffondeva in tutto il citoplasma.
Le ecoLNP alla Prova In Vivo: Risultati Promettenti
Dopo i successi in vitro, era il momento di testare le ecoLNP in modelli animali (topi C57BL/6). Abbiamo provato diverse vie di somministrazione:
- Endovenosa (IV): L’mRNA si è accumulato principalmente nel fegato e nella milza.
- Sottocutanea (SC) e Intramuscolare (IM): Forte espressione proteica nel sito di iniezione. Sorprendentemente, con l’iniezione IM, abbiamo osservato un notevole tropismo per i linfonodi! Questa è una notizia fantastica per l’immunoterapia e i vaccini, dato che i linfonodi sono centri nevralgici del sistema immunitario.
- Altre vie locali: Abbiamo testato anche iniezioni sottocongiuntivali (SCJ) e sottoretiniche (SR) per l’occhio, e instillazioni intravescicali (IVS) per la vescica, ottenendo in tutti i casi un’espressione proteica specifica nel tessuto bersaglio.
Le ecoLNP hanno mostrato un’attività dose-dipendente e, dopo somministrazione IV, l’espressione proteica nel fegato e nella milza era robusta già dopo 2 ore, rimanendo elevata per almeno 8 ore e rilevabile fino a quasi 3 giorni. Importante, non abbiamo osservato effetti tossici significativi a livello di fegato, reni o altri parametri ematici, né alterazioni patologiche nei tessuti principali.
Un confronto diretto con le LNP SM-102 (quelle usate nel vaccino Moderna) per iniezione intramuscolare ha rivelato che le nostre ecoLNP hanno una potenza di delivery comparabile, ma un tropismo per i linfonodi significativamente maggiore (90.2% vs 58.1%). Questo potrebbe tradursi in risposte immunitarie più efficaci.
Editing Genomico con le ecoLNP: Il Futuro è Adesso?
Per spingerci oltre, abbiamo voluto vedere se le ecoLNP potessero essere usate per l’editing genomico. In topi reporter Ai9 (che esprimono una proteina fluorescente rossa, tdTomato, solo dopo una specifica modifica genetica), abbiamo iniettato ecoLNP cariche di mRNA per l’enzima Cre ricombinasi. La Cre è in grado di “tagliare” una sequenza “stop” nel DNA dei topi, attivando l’espressione di tdTomato. Ebbene, abbiamo osservato un aumento di 4.7 volte della fluorescenza rossa nei siti di iniezione e nei linfonodi, confermando il successo dell’editing!
Non contenti, abbiamo alzato l’asticella: co-delivery di mRNA per Cas9 (le “forbici molecolari” di CRISPR) e un gRNA (la “guida” che dice a Cas9 dove tagliare), mirando a tre siti ripetuti nella cassetta stop. Questo è tecnicamente più complesso, ma anche in questo caso abbiamo ottenuto l’attivazione dell’espressione di tdTomato, segno di un editing genomico riuscito! L’analisi di sequenziamento ha confermato diversi tipi di modifiche genetiche nei siti bersaglio.
Cosa Abbiamo Imparato e Dove Andiamo?
Questo studio ci ha insegnato molto sulla progettazione razionale di lipidi per il delivery di mRNA. Piccole variazioni strutturali possono avere grandi impatti. L’anello di chinolina è cruciale, così come il giusto tipo di sostituenti e il numero corretto di atomi di azoto ionizzabili nel linker. È una sinergia tra i tre “mattoncini” (scaffold, linker, code) a determinare l’efficacia.
Le ecoLNP rappresentano, a mio avviso, una piattaforma di delivery versatile e potente, con un meccanismo di fuga endosomiale ben definito e un promettente profilo di sicurezza ed efficacia in vivo, incluso un interessante tropismo linfonodale. Il fatto che possano essere conservate a 4°C è un ulteriore vantaggio logistico non da poco.
Certo, la ricerca non si ferma qui. Un prossimo passo sarà progettare versioni biodegradabili di questi lipidi, per migliorarne ulteriormente il profilo di sicurezza a lungo termine. Ma la strategia di design modulare guidata dalla struttura, che abbiamo presentato, apre la strada alla creazione di sistemi di delivery di mRNA di nuova generazione, sempre più efficienti e specifici.
È un campo in continua evoluzione, e ogni piccolo passo avanti ci avvicina a terapie rivoluzionarie per malattie che oggi sembrano incurabili. E io, nel mio piccolo, sono entusiasta di far parte di questa avventura!
Nota: L’articolo scientifico originale a cui si fa riferimento nel testo fornito è “Structure-guided design of endosomolytic chloroquine-like lipid nanoparticles for mRNA delivery and genome editing” con DOI che termina in s41467-024-49501-y. Il link fornito per la fonte (s41467-025-59501-y) potrebbe riferirsi a una versione corretta, a un articolo correlato o a un errore di battitura nel prompt. Ho basato il contenuto sull’abstract e sul testo fornito che sembrano allineati con il titolo dell’articolo.